各位老师们在处理测序或者芯片数据的时候,经常会用到PCA分析。但PCA分析虽好,也并非万能,尤其对于微生物多样性等数据来说,当样本量大且影响样本分类的环境因素过多的时候,PCA分类效果可能相对就不会太好。这时候我们往往推荐PCoA或者NMDS,这些基于距离矩阵算法的分析。
本文通过介绍欧易云PCoA分析工具,让您轻松get新技能。
PCoA基本概念
PCoA(Principal Co-ordinates Analysis)是一种研究数据相似性或差异性的可视化方法,通过一系列的特征值和特征向量进行排序后,选择主要排在前几位的特征值。通过PCoA 可以观察个体或群体间的差异。
PCoA分析操作步骤
通过传送门快速进入分析界面:https://cloud.www.oebiotech.com/task/detail/principal_co-ordinates_analysis/
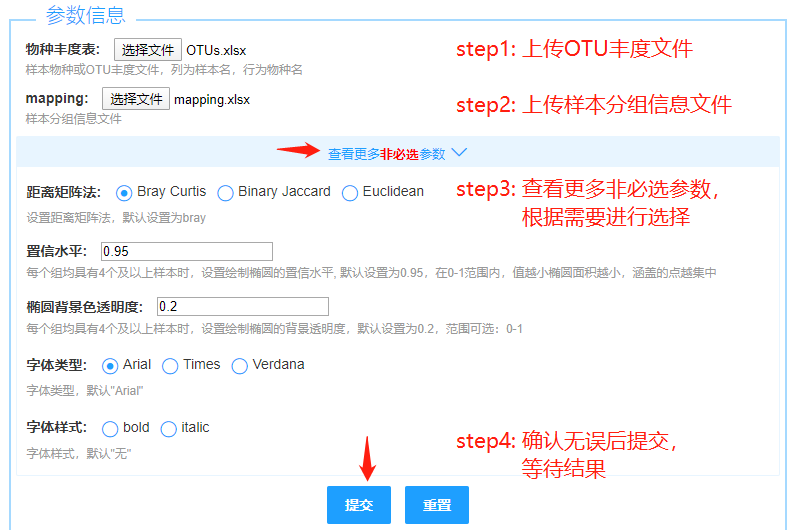
Step1
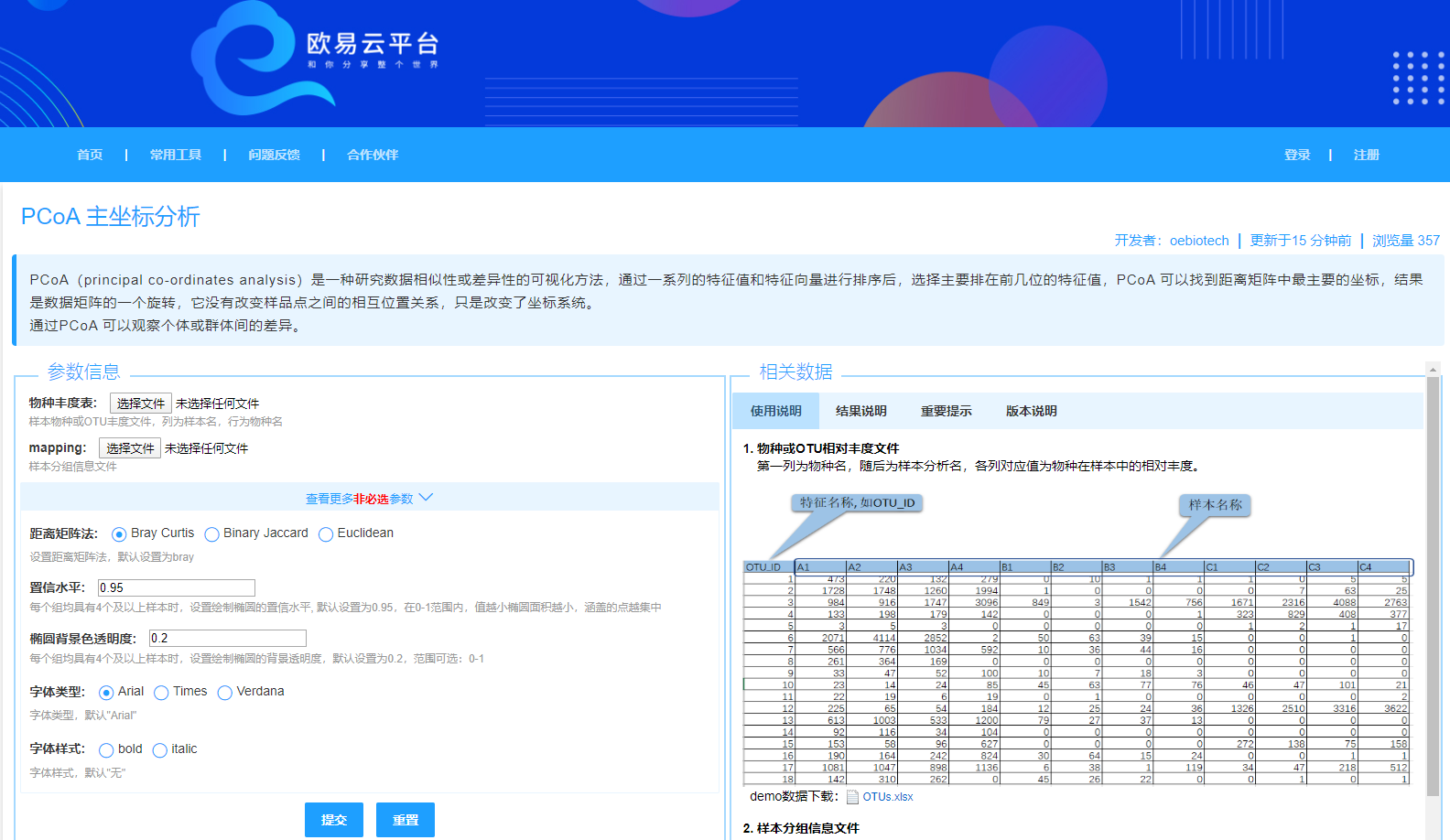
上传OTU或物种相对丰度文件,文件支持读取txt、xls、xlsx、csv格式:
(1) OTU丰度文件示例:
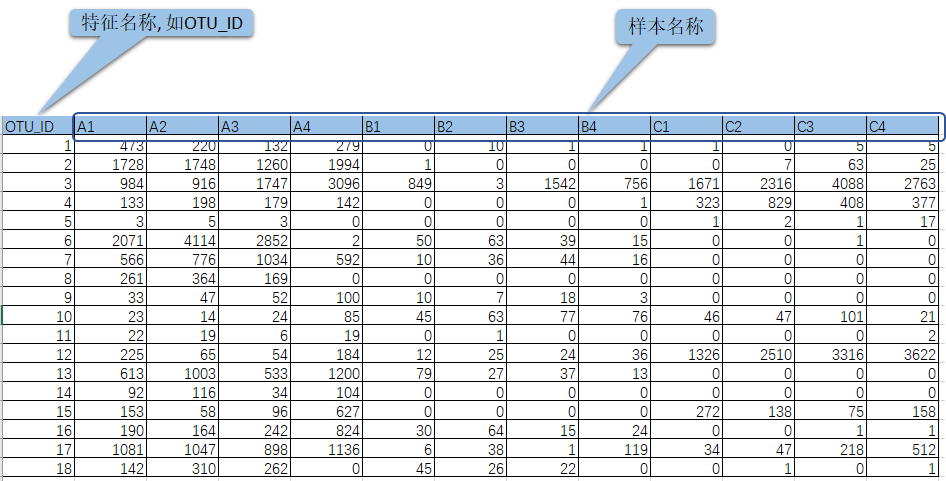
(2) 物种相对丰度文件示例:
Step2
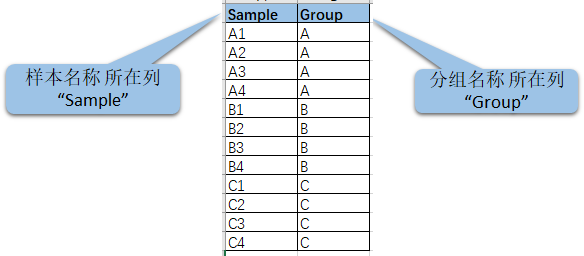
上传样本分组信息文件:
样品分组信息通常包含两列,第一列为样品分析名;第二列为样本的分组名称,表头必须命名为“Group”方可被工具识别。
Step3
其他更多非必选参数选择:
(1) 距离矩阵法:(默认设置为Bray Curtis)
① Bray Curtis: 距离算法,考虑物种的丰度;
② Binary Jaccard: 距离算法,仅仅考虑物种的有无,不考虑物种的丰度(非加权算法)。
Jaccard 系数,又叫 Jaccard 相似性系数,用来比较样本集中的相似性和分散性的一个概率;
③ Euclidean: 欧式距离算法,考虑物种的丰度(加权算法)。
欧氏距离(Euclidean distance)是一个通常采用的距离定义,它是在 m 维空间中两个点之间的真实距离。
(2) 置信水平:(默认设置为0.95)
设置绘制椭圆的置信水平。在0-1范围内,值越小椭圆面积越小,涵盖的点越集中。
注意:每个组均具有4个及以上样本才能加置信椭圆。
(3) 椭圆背景色透明度: (默认设置为0.2)
设置绘制椭圆的背景透明度,范围可选:0-1。
(4) 字体类型: (默认设置为Arial)
可选择Arial、Times、Verdana。
(5) 字体样式: (默认设置为“无”)
可选择bold、italic。
Step4
点击“提交”按钮,提交任务即可等待结果输出。
PCoA分析结果查看。
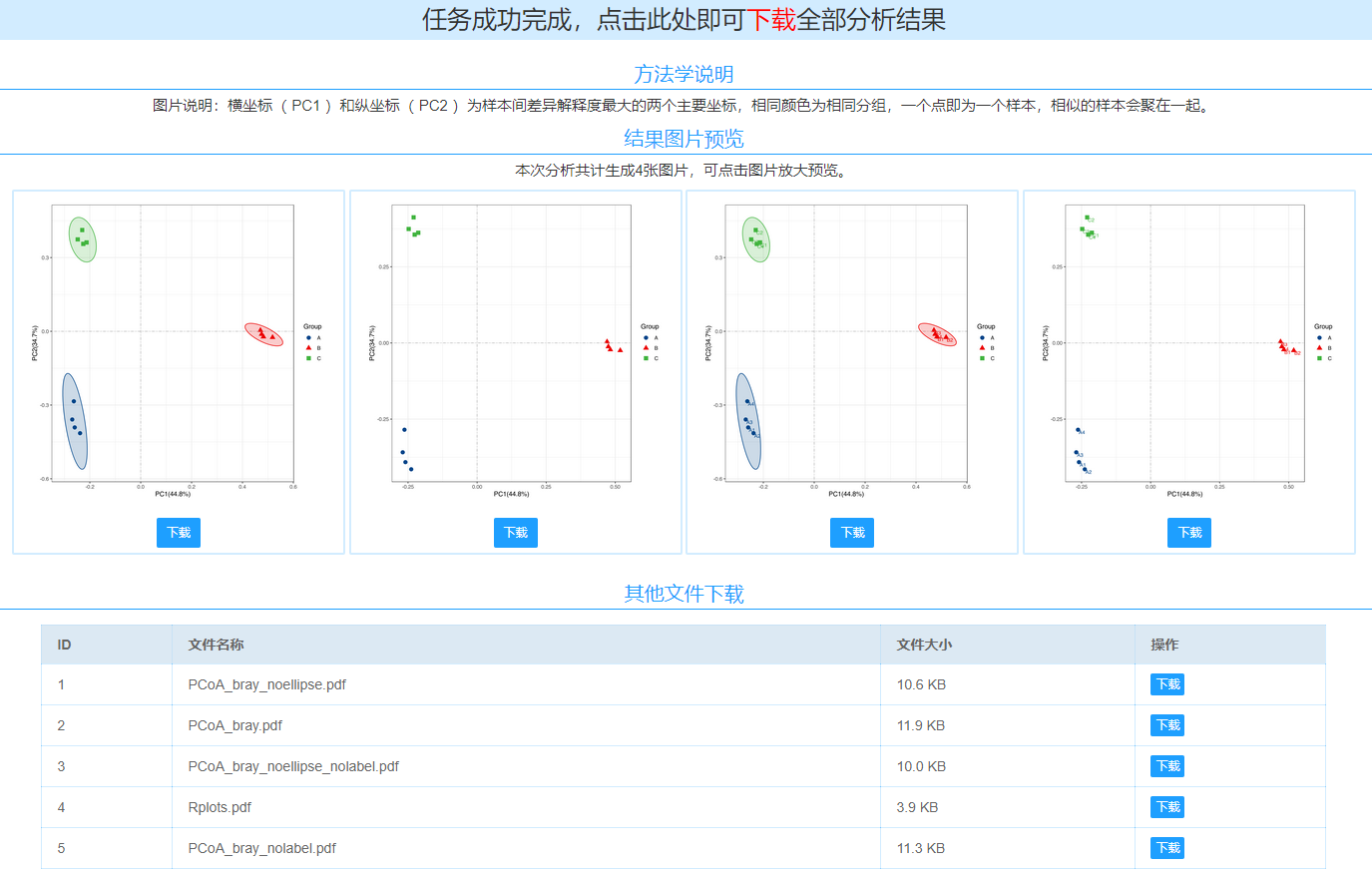
工具成功运行后生成PCoA的2D图。
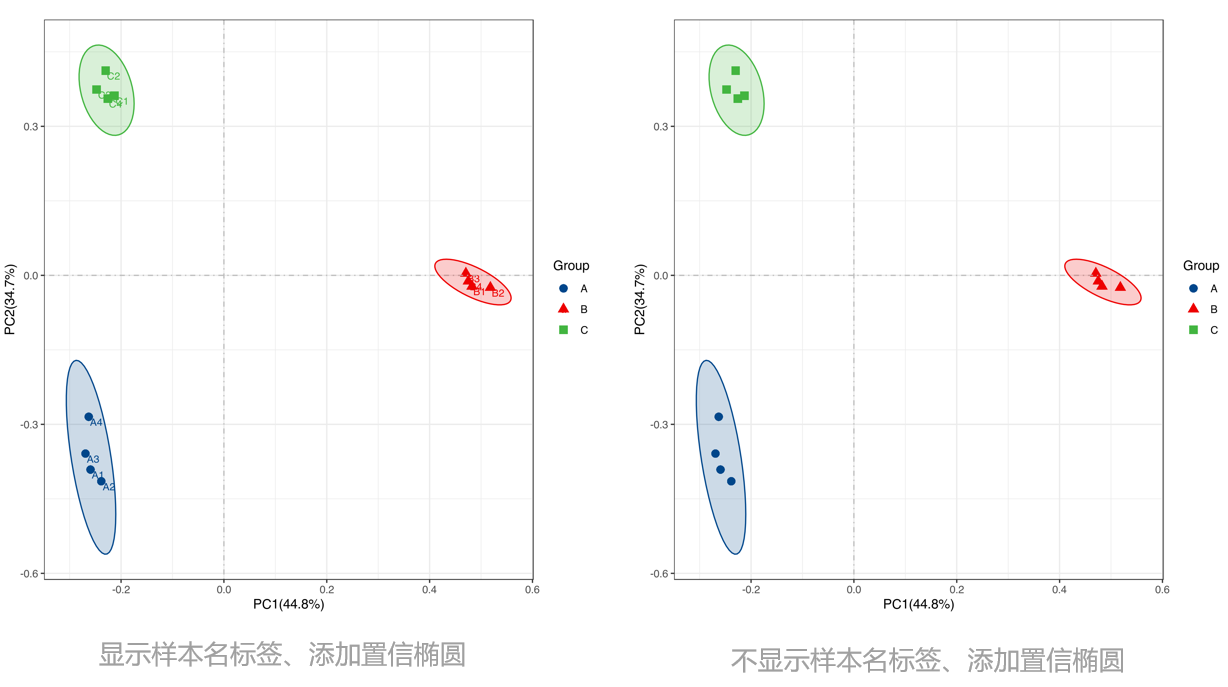
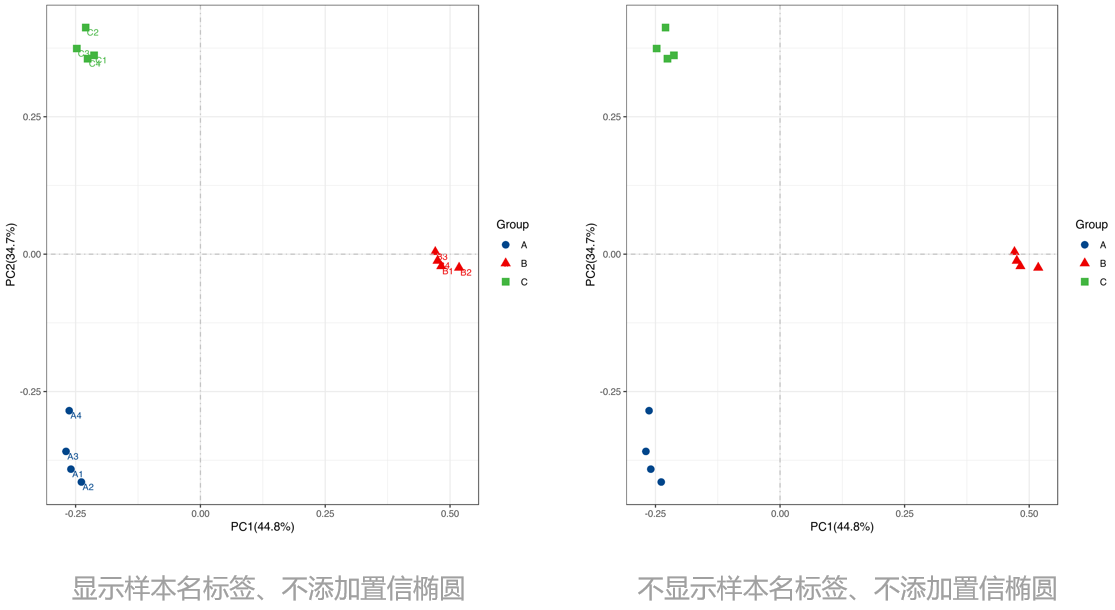
PCoA(2D)图:横坐标(PC1)和纵坐标(PC2)为样本间差异解释度最大的两个主要坐标,相同颜色为相同分组,一个点即为一个样本,越相似的样本距离会越近。当每组样本数≥4时,2D结果图会同时提供添加置信椭圆和不添加置信椭圆的作图结果;当每组样本数<4时,2D结果仅提供不添加置信椭圆的作图结果,并且会生成显示样本名标签和不显示样本名标签的结果。
本次欧易云主成分分析PCoA小工具推荐到此结束啦,欢迎各位使用并提供反馈(点击网页上方的“问题反馈”),我们会持续更新,竭诚为您提供最优质的服务。






